У нас юбилей!

Программное обеспечение HistoQuest сочетает в себе классические функции, включая автоматическое разделение цветов, и новые, например, сравнение изображений. Поддержка многооконности, возможность вывода на дисплей большого количества данных одновременно и экспорт функций делают ПО HistoQuest полноценным исследовательским и диагностическим инструментом.
Основные особенности
Автоматическое и полуавтоматическое разделение по цветам
Для анализа иммуногистохимические изображения должны быть разделены по цветам. HistoQuest обеспечивает два режима работы - полностью автоматизированное разделение по двум маркерам или полуавтоматическое разделение по дополнительным маркерам.
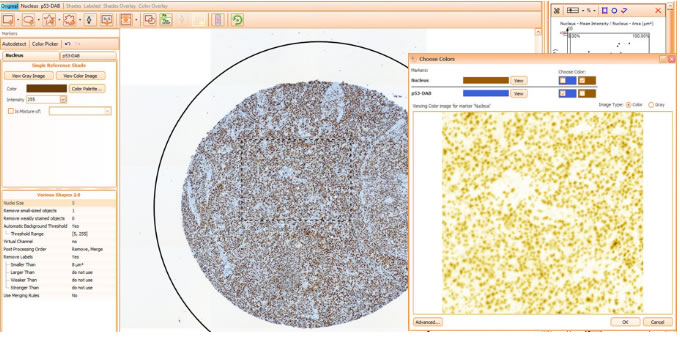
Автоматический режим позволяет очень быстро получить результат, полуавтоматический режим предоставляет возможности для более тонкой настройки. Чем больше цветов указано, тем точнее будут результаты исследования.
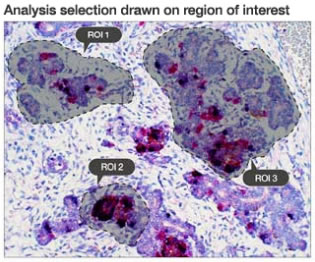
Регионы интересов (ROI), исключенные регионы и аннотации
Для дифференцированного анализа на слайде могут быть указаны регионы интереса и регионы, которые можно исключить из анализа. Эти поля могут быть указаны пользователем. Возможно создание аннотаций в различных форматах.
Загрузка и импорт проектов сканирования
HistoQuest 3.5 позволяет проводить анализ проектов, не только созданных в системах TissueFAXS/HistoFAXS, но и изображений образцов, полученных из других источников. Для анализа могут быть импортированы цифровые слайды, созданные в сканерах Mirax, Pannoramica и Hamamatsu.
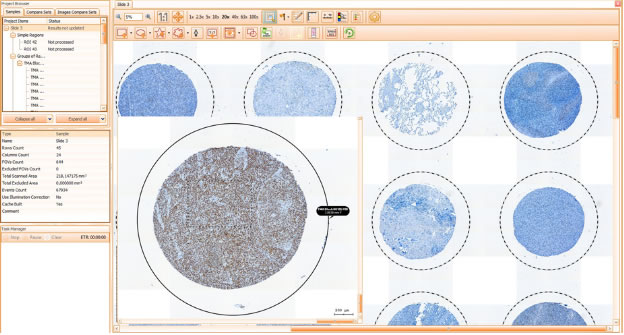
TMA анализ
Полная поддержка анализа TMA (тканевых микросрезов). Проекты, созданные в системах TissueFAXS/HistoFAXS, уже содержат споты ТМА, собранные в столбцы. Для пользователей, которым необходимо анализировать импортированные ТМА проекты с других сканеров в программное обеспечение, могут быть интегрированы модули автоматической или ручной маркировки ID.
Автоматизация
HistoQuest 3.5 позволяет работать с несколькими образцами в рамках одного проекта (до 12 в зависимости от размера выборки) и анализировать их параметры по профилям, созданным при работе с первым образцом. Профили для цветоразделения и настройки сегментации могут быть повторно использованы для дальнейшего анализа образцов.
Новые параметры измерений
В текущей версии HistoQuest добавлены новые расчетные и процентные параметры измерений интенсивности окрашенности областей.
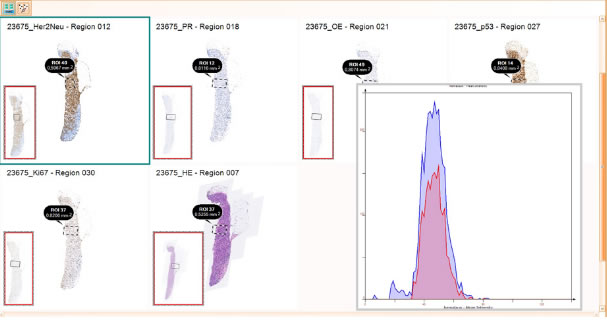
Сравнительный анализ изображений
В системе может быть проведён сравнительный анализ одних и тех же участков, окрашенных разными маркерами.
Сравнительный анализ данных
Может быть проведено сравнение графических изображений (скатерограмм, гистограмм) способами сопоставления и наложения.
Экспорт данных
Поддерживаются 3 режима экспорта данных.
Ниже представлена общая таблица, содержащая все данные анализируемых объектов.
Печатный отчет обеспечивает быстрый обзор проекта и показывает все соответствующие графики и статистические данные проекта. Этот отчет можно экспортировать в различные форматы.
Статистический отчет позволяет выделить определенные наборы данных по нескольким проектам.
Обработка изображений никогда не была такой легкой
Модульность
HistoQuest имеет модульную структуру, позволяющую скомпоновать пакет программного обеспечения под задачи конкретного пользователя.
Модуль 1 – для подсчета клеток
Модуль 2 – для автоматического подсчета клеток
Модуль 3 – диагностирующий
Модуль 4 - диагностика Xtended
Модуль 5 - TMA
Система сравнения и сопоставления
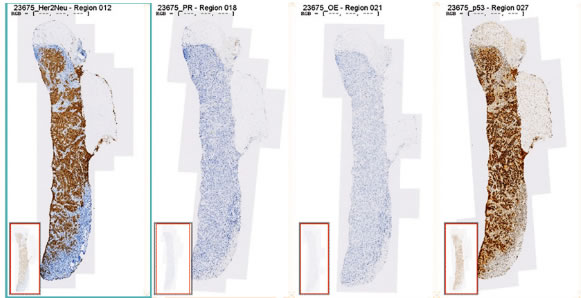
Для оптимального сравнения результатов анализа в одной и той же анатомической структуре можно наложить друг на друга до 6 снимков одного образца с различными методиками окрашивания.
Загрузка проектов и импорт изображений
В HistoQuest возможно загрузить полные проекты, созданные в системе HistoFAXS .
При наличии слайда всегда можно связать проект с реальным слайдом.
Кроме того, можно работать с отдельными изображениями, полученными из других источников, без привязки к реальному слайду.
Цветоделение
В отличие от иммунофлуоресценции маркер информации в иммуногистохимических изображениях, содержится в самом изображении, поэтому для того, чтобы провести анализ, необходимо произвести цветоделение. HistoQuest даёт возможность выбора из нескольких вариантов цветоделения:
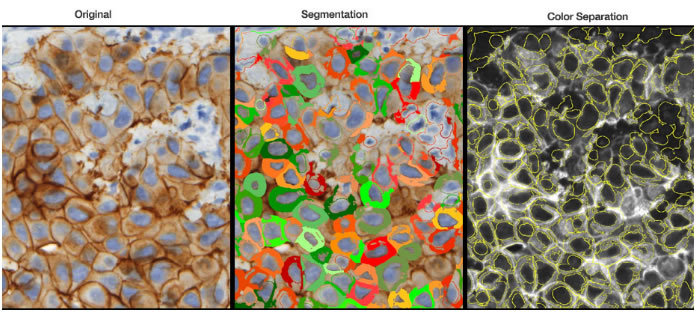
Ядерная сегментация
TissueGnostics имеет запатентованные алгоритмы для автоматической ядерной сегментации.
Для того, чтобы провести ядерную сегментацию, необходимо ввести несколько пороговых значений:

Визуальный контроль
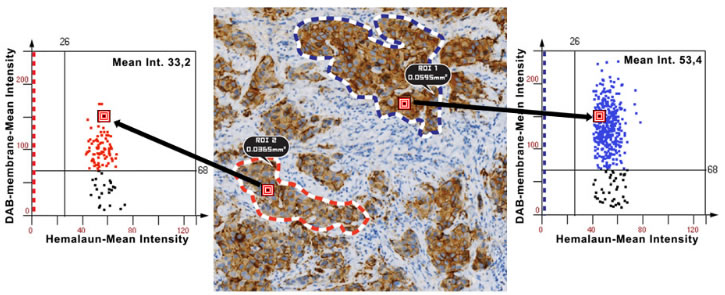
HistoQuest предлагает инновационные функции для визуального контроля и измерения.
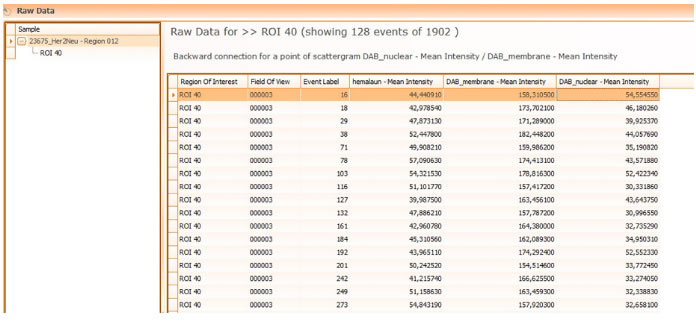
Взаимосвязь точки скатерограммы и определённой клетки на изображении позволяет пользователю найти точку, соответствующую конкретной клетке, и наоборот.
Функция «Просмотр событий данных» считывает все данные измерений для отдельных клеток.
Раздел не найден


